R语言学习 - 非参数法生存分析
微信公众号:http://blog.genesino.com
生存分析指根据试验或调查得到的数据对生物或人的生存时间进行分析和推断,研究生存时间和结局与众多影响因素间关系及其程度大小的方法,也称生存率分析或存活率分析。常用于肿瘤等疾病的标志物筛选、疗效及预后的考核。
简单地说,比较两组或多组人群随着时间的延续,存活个体的比例变化趋势。活着的个体越少的组危险性越大,对应的基因对疾病影响越大,对应的药物治疗效果越差。
生存分析适合于处理时间-事件数据,如下
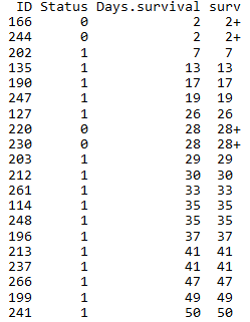
生存时间数据有两种类型:
- 完全数据 (complete data)指被观测对象从观察起点到出现终点事件所经历的时间; 一般用状态值1或TRUE表示。
- 截尾数据 (consored data)或删失数据,指在出现终点事件前,被观测对象的观测过程终止了。由于被观测对象所提供的信息是不完全的,只知道他们的生存事件超过了截尾时间。截尾主要由于失访、退出和终止产生。一般用状态值0或FALSE表示。
- TCGA中的临床数据标记也符合这个规律,在下面软件运行时也可修改状态值的含义, 但一般遵循这个规律。
生存概率 (survival probability)指某段时间开始时存活的个体至该时间结束时仍然存活的可能性大小。
生存概率=某人群活过某段时间例数/该人群同时间段期初观察例数。
生存率 (Survival rate),用S(t)表示,指经历t个单位时间后仍存活的概率,若无删失数据,则为活过了t时刻仍然存活的例数/观察开始的总例数。如果有删失数据,分母则需要按时段进行校正。
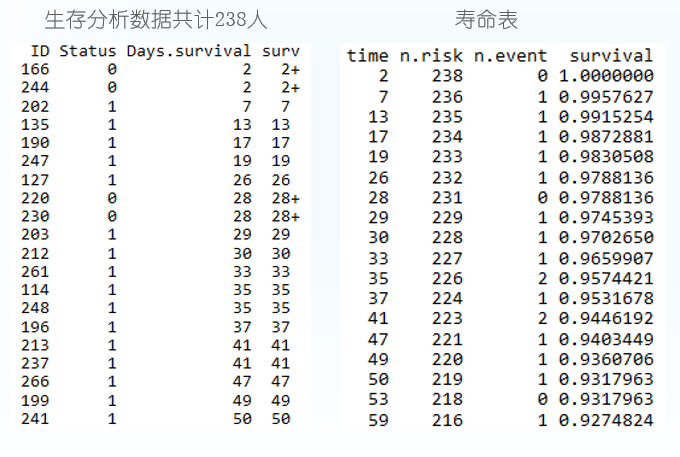
生存分析一个常用的方法是寿命表法。
寿命表是描述一段时间内生存状况、终点事件和生存概率的表格,需计算累积生存概率即每一步生存概率的乘积 (也可能是原始生存概率),可完成对病例随访资料在任意指定时点的生存状况评价。
R做生存分析
R中做生存分析需要用到包survival和survminer。输入数据至少两列,存活时间和生存状态,也就是测试数据中的Days.survial和vital_status列。如果需要比较不同组之间的差异,也需要提供个体的分组信息,如测试数据中的PAM50列。对应TCGA的数据,一般根据某个基因的表达量或突变有无对个体进行分组。
读入数据
library(survival)
BRCA <- read.table('BRCA.tsv', sep="\t", header=T)
head(BRCA) ID SampleType PAM50Call_RNAseq Days.survival pathologic_stage
1 TCGA-E9-A2JT-01 Tumor_type LumA 288 stage iia
2 TCGA-BH-A0W4-01 Tumor_type LumA 759 stage iia
3 TCGA-BH-A0B5-01 Tumor_type LumA 2136 stage iiia
4 TCGA-AC-A3TM-01 Tumor_type Unknown 762 stage iiia
5 TCGA-E9-A5FL-01 Tumor_type Unknown 24 stage iib
6 TCGA-AC-A3TN-01 Tumor_type Unknown 456 stage iibvital_status
1 0
2 0
3 0
4 0
5 0
6 0简单地看下每一列都有什么内容,方便对数据整体有个了解,比如有无特殊值。
summary(BRCA) ID SampleType PAM50Call_RNAseq Days.survival TCGA-3C-AAAU-01: 1 Tumor_type:1090 Basal :138 Min. : 0.0 TCGA-3C-AALI-01: 1 Her2 : 65 1st Qu.: 450.2 TCGA-3C-AALJ-01: 1 LumA :415 Median : 848.0 TCGA-3C-AALK-01: 1 LumB :194 Mean :1247.0 TCGA-4H-AAAK-01: 1 Normal : 24 3rd Qu.:1682.8 TCGA-5L-AAT0-01: 1 Unknown:254 Max. :8605.0 (Other) :1084 pathologic_stage vital_status stage iia :359 Min. :0.0000 stage iib :259 1st Qu.:0.0000 stage iiia:156 Median :0.0000 stage i : 90 Mean :0.1394 stage ia : 85 3rd Qu.:0.0000 stage iiic: 67 Max. :1.0000 (Other) : 74 计算寿命表
# Days.survival:跟踪到的存活时间
# vital_status: 跟踪到的存活状态
# ~1表示不进行分组
fit <- survfit(Surv(Days.survival, vital_status)~1, data=BRCA)# 获得的survial列就是生存率
summary(fit)Call: survfit(formula = Surv(Days.survival, vital_status) ~ 1, data = BRCA)time n.risk n.event survival std.err lower 95% CI upper 95% CI116 1021 1 0.999 0.000979 0.997 1.000158 1017 1 0.998 0.001386 0.995 1.000160 1016 1 0.997 0.001697 0.994 1.000172 1010 1 0.996 0.001962 0.992 1.000174 1008 1 0.995 0.002195 0.991 0.999197 1003 1 0.994 0.002406 0.989 0.999224 993 1 0.993 0.002604 0.988 0.998227 990 1 0.992 0.002788 0.987 0.998239 987 1 0.991 0.002961 0.985 0.997255 981 1 0.990 0.003125 0.984 0.996266 978 1 0.989 0.003282 0.983 0.996295 965 1 0.988 0.003435 0.981 0.995302 962 1 0.987 0.003581 0.980 0.994304 958 1 0.986 0.003723 0.979 0.993320 948 1 0.985 0.003862 0.977 0.993322 946 1 0.984 0.003995 0.976 0.992绘制生存曲线,横轴表示生存时间,纵轴表示生存概率,为一条梯形下降的曲线。下降幅度越大,表示生存率越低或生存时间越短。
library(survminer)
# conf.int:是否显示置信区间
# risk.table: 对应时间存活个体总结表格
ggsurvplot(fit, conf.int=T,risk.table=T)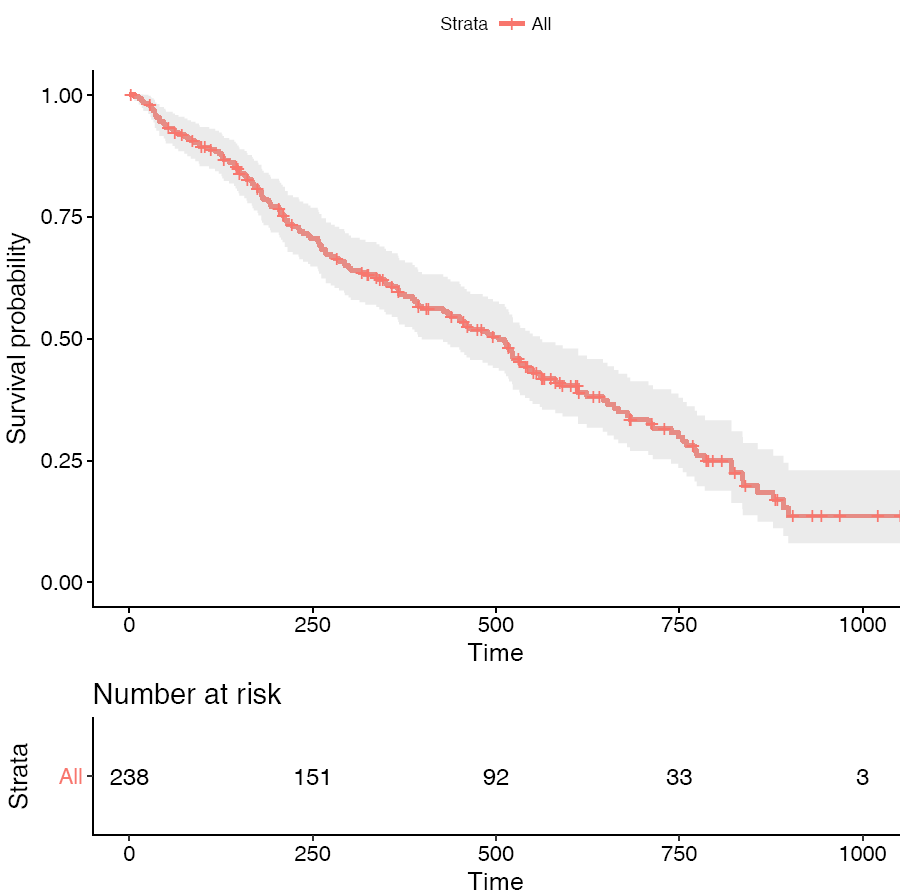
PAM50是通过50个基因的表达量把乳腺癌分为四种类型 (Luminal A, Luminal B, HER2-enriched, and Basal-like)作为预后的标志。根据PAM50属性对病人进行分组,评估比较两组之间生存率的差别。
# 这三步不是必须的,只是为了方便,选择其中的4个确定了的分组进行分析
# 同时为了简化图例,给列重命名一下,使得列名不那么长
BRCA_PAM50 <- BRCA[grepl("Basal|Her2|LumA|LumB",BRCA$PAM50Call_RNAseq),]
BRCA_PAM50 <- droplevels(BRCA_PAM50)
colnames(BRCA_PAM50)[colnames(BRCA_PAM50)=="PAM50Call_RNAseq"] <- 'PAM50'
# 按PAM50分组
fit <- survfit(Surv(Days.survival, vital_status)~PAM50, data=BRCA_PAM50)
# 绘制曲线
ggsurvplot(fit, conf.int=F,risk.table=T, risk.table.col="strata", pval=T)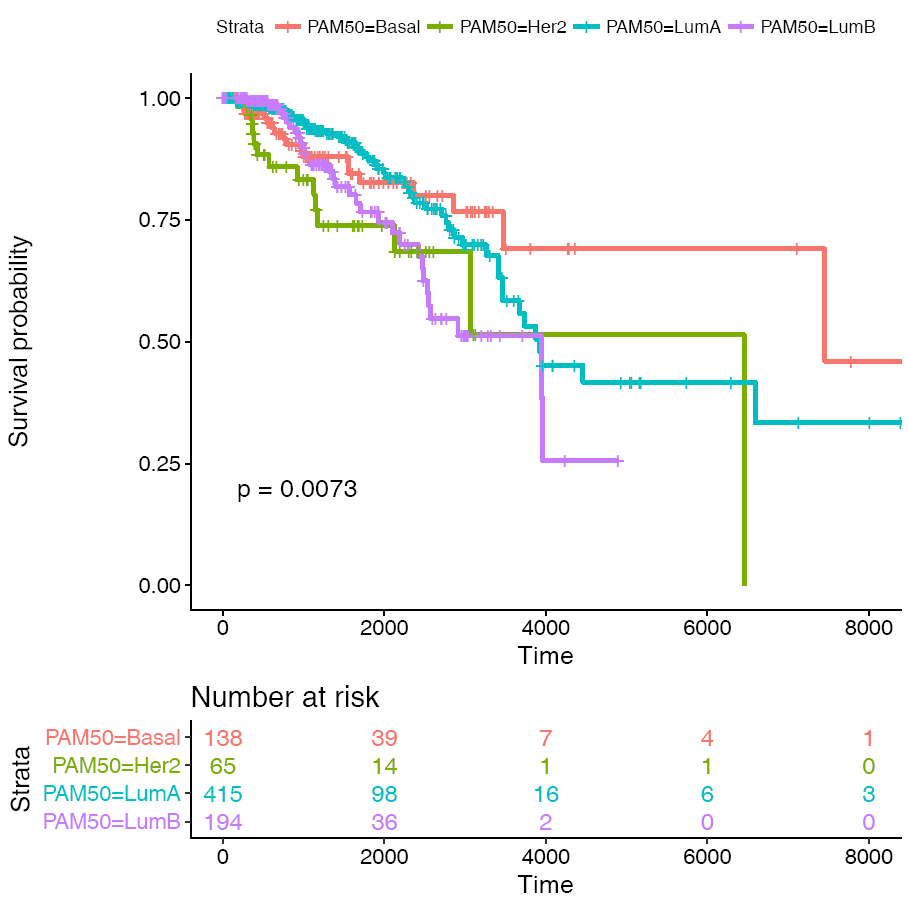
简化Stage信息,先只查看大的阶段
BRCA_PAM50$pathologic_stage <- gsub('(i+v*).*', "\\1", BRCA_PAM50$pathologic_stage)
BRCA_PAM50$pathologic_stage <- as.factor(BRCA_PAM50$pathologic_stage)
colnames(BRCA_PAM50)[colnames(BRCA_PAM50)=="pathologic_stage"] <- 'PS'
fit <- survfit(Surv(Days.survival, vital_status)~PS, data=BRCA_PAM50)
# 绘制曲线
ggsurvplot(fit, conf.int=F,risk.table=T, risk.table.col="strata", pval=T)参考资料
- http://rpubs.com/xuefliang/153247
- http://www.sthda.com/english/wiki/survminer-r-package-survival-data-analysis-and-visualization
R语言学习 - 非参数法生存分析相关推荐
- R语言学习 - 非参数法生存分析--转载
生存分析指根据试验或调查得到的数据对生物或人的生存时间进行分析和推断,研究生存时间和结局与众多影响因素间关系及其程度大小的方法,也称生存率分析或存活率分析.常用于肿瘤等疾病的标志物筛选.疗效及预后的考 ...
- R语言Kaplan-Meier绘制生存分析、Log-rank假设检验、Cox回归曲线实战案例:恶性黑色素瘤的术后数据生存分析
R语言Kaplan-Meier绘制生存分析.Log-rank假设检验.Cox回归曲线实战案例:恶性黑色素瘤的术后数据生存分析 目录
- R语言rms包生存分析之限制性立方样条(RCS, Restricted cubic spline)分析详解实战:拟合连续性自变量和事件风险之间的关系:基于survival包lung数据
R语言rms包生存分析之限制性立方样条(RCS, Restricted cubic spline)分析详解实战:拟合连续性自变量和事件风险之间的关系:基于survival包lung数据 目录
- R语言rms包生存分析之限制性立方样条(RCS, Restricted cubic spline)分析:拟合连续性自变量和事件风险之间的关系并绘制直方图、平滑曲线、双Y轴于同一个图像中
R语言rms包生存分析之限制性立方样条(RCS, Restricted cubic spline)分析:拟合连续性自变量和事件风险之间的关系并绘制直方图.平滑曲线.双Y轴于同一个图像中 目录
- R语言教程:生存分析
生存分析处理预测特定事件将要发生的时间.它也被称为故障时间分析或分析死亡时间.例如,预测患有癌症的人将存活的天数或预测机械系统将失败的时间. 命名为survival的R语言包用于进行生存分析.此包包含 ...
- R语言学习(六)——关联规则分析
什么是关联规则 引例:啤酒与尿布 发现了买尿布的顾客经常也会买啤酒后,超市把两者摆在一起,从而提高了两者的销量.具体原因是:年轻的父亲下班回家的路上需要给孩子买尿布,但他们又没空去酒吧,所以就通常也给 ...
- R语言如何在生存分析与Cox回归中计算IDI,NRI指标
在诊断试验中,我们比较两个模型的优劣时,除了可以比较两个模型roc外,还可以用定量的指标来比较一个模型比另外一个模型诊断准确率改进的程度.我们围绕生存分析技术进行一些咨询,帮助解决独特的业务问题. ...
- 用R语言进行KM生存分析
欢迎关注"生信修炼手册"! R是数据分析常用的软件之一,通过各种功能强大的R包,可以简单方便的实现各种分析.在R语言中,能够进行生存分析的R包很多,survival和survmin ...
- R语言学习 - 热图简化
前面推出过热图绘制和热图美化,现在来一个函数绘制热图的简化方式.文后更有不用写代码的在线工具可用. R语言 - 基础概念和矩阵操作 R语言 - 热图简化 R语言 - 热图绘制 (heatmap) R语 ...
最新文章
- STM32 基础系列教程 41 – SDMMC
- python 一个列表转字典_python基础语法:列表和字典
- ASP.NET Core 6 Minimal API
- Linux操纵零碎下设置JSP开发环境的方式
- JUC:ConcurrentSkipListMap/ConcurrentSkipListSet(并发容器)
- .aspx IIS发布404.17时候的问题
- JSP中报错only a type can be imported XXX resolves to package
- [Android] SharedPreferences(轻量级的存储方式)
- vba html 教程 pdf,Word VBA教程:CanvasShapes集合
- JAVA使用JEP进行动态公式计算
- 计算机组成原理:P5-存储器(下)
- HTML5+CSS大作业——年会抽奖网页设计(1页)
- 滑动窗口(java)
- 工作展望简短_简短的工作计划
- 【Python】官方文档中文版
- kafka 报错: IllegalArgumentException: Error creating broker listeners from ‘PLAINTEXT:xxx.xxx.xxx.xx
- VMware拟收购云应用管理服务商Wavefront
- Sen2Cor-02.05.05处理哨兵数据的坑
- Python-opencv实现Trackbar调节亮度对比度
- SAP BAPI BAPI_PO_CREATE1创建采购订单
